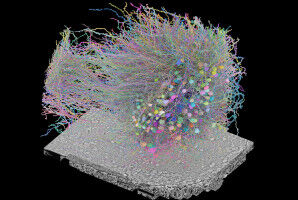
Une cartographie spatiale de l’expression génique
- EN- FR
Les chercheurs de l'EPFL ont développé un algorithme capable de représenter l'organisation spatiale de l'expression génique dans le corps tout en se dispensant des microscopes ou de l'équipement complexe actuellement nécessaires. À mesure que nous accumulons de plus en plus d'informations sur le séquençage des gènes, la taille et la complexité des bases de données de types cellulaires s'accroissent. Il devient nécessaire de comprendre où les différents types de cellules sont situés dans le corps, et de cartographier l'organisation de l'expression de leurs gènes en fonction de leur emplacement précis dans les différents tissus et organes. En effet, un gène peut être exprimé activement dans une cellule et réprimé dans une autre. L'une des méthodes de cartographie des gènes dans les tissus repose sur la technique appelée hybridation in situ . Pour simplifier, un gène cible est marqué («hybridé») avec un marqueur fluorescent dans les coupes du tissu où il se trouve (« in situ »). Les coupes de tissu sont ensuite observées à l'aide d'un microscope spécial permettant de voir les endroits où le gène «s'éclaire». Les photographies consécutives de chaque coupe sont alors rassemblées pour générer une carte «spatiale» de l'emplacement du gène dans le tissu. Le problème des méthodes utilisant l'hybridation in situ tient au fait que lorsque le nombre de gènes cibles augmente, leur complexité s'accentue, un équipement spécial devient nécessaire et les chercheurs sont amenés à sélectionner leurs cibles en amont, processus pouvant s'avérer laborieux si l'objectif est de reconstruire une carte complète de la répartition des gènes dans les tissus. « Organisation spatiale» des données de séquençage