Eine an der EPFL entwickelte Computermethode ermöglicht es, den Einfluss von Wasser bei der Entwicklung von Membranrezeptoren mit verbesserter Stabilität und Signalgebung explizit zu berücksichtigen.
Proteine sind die Motoren des Lebens, die Prozesse wie Muskelbewegungen, Sehen und chemische Reaktionen antreiben. Ihre Umgebung - Wasser, Lipidmembranen oder andere kondensierte Phasen - ist für ihre Funktion von entscheidender Bedeutung und prägt ihre Struktur und Interaktionen.
Dennoch lassen viele moderne Methoden des Proteindesigns, einschließlich KI-gestützter Tools, oftmals den Einfluss dieser Umgebungen auf die Proteine außer Acht. Dies schränkt unsere Fähigkeit ein, Proteine mit neuen Funktionen zu entwickeln, und bremst damit mögliche Fortschritte.
Membranrezeptoren sind eine Gruppe von Proteinen, die besonders empfindlich auf ihre spezifische Umgebung reagieren. Wie biologische "Antennen" nehmen sie Signale aus der Umwelt auf und lösen dadurch zelluläre Reaktionen aus.
Gerade die G-Protein-gekoppelten Rezeptoren (GPCRs) spielen eine zentrale Rolle dabei, wie Zellen externe Reize wahrnehmen und wie sie darauf reagieren. Um ihre Signalisierung durchzuführen, verlassen sich GPCRs auf ein empfindliches Zusammenspiel zwischen struktureller Stabilität, Flexibilität und Ligandenbindung, ein Ausgleich, der oft durch Wasser vermittelt wird. Diese Interaktionen ermöglichen es GPCRs, ihre Form zu verändern und die Signale, die sie empfangen, an die Zelle weiterzugeben.
Die Bedeutung dieser molekularen Wächter für die Zellfunktion ist so groß, dass etwa ein Drittel aller Medikamente auf dem Markt auf sie abzielt. Auch die Proteinentwicklung konzentriert sich auf sie, um diese Rezeptoren zu verändern, um die Wirksamkeit von Medikamenten zu verbessern, neue Behandlungsmethoden zu entwickeln oder sie sogar als Biosensoren in der synthetischen Biologie wiederzuverwenden.
Was ist das Problem? GPCRs sind unglaublich komplex und ihre subtile Abhängigkeit von Wasser macht es unmöglich, sie auf vernünftige Weise herzustellen - bis jetzt.
Ein Team unter der Leitung von Patrick Barth, Professor am Labor für Protein- und Zelltechnik der EPFL, hat Computertools entwickelt, die in der Lage sind, die Skala der wasserstreuenden Wechselwirkungen von GPCRs zu verändern, um neue Membranrezeptoren zu entwerfen, die leistungsfähiger sind als ihre natürlichen Gegenstücke. Die in Nature Chemistry veröffentlichten Arbeiten ebnen den Weg für leistungsfähigere Medikamente und neue Werkzeuge in der synthetischen Biologie.
"Wasser ist allgegenwärtig", erklärt Lucas Rudden, Hauptmitautor der Studie. "Es ist die unerkannte Heldin der Proteinfunktion und wird beim Design oft übersehen, insbesondere wenn es um die Allosterie von Membranrezeptoren geht, da es schwer explizit zu modellieren ist. Wir wollten eine Methode entwickeln, die in der Lage ist, neue Sequenzen zu entwerfen und gleichzeitig den Einfluss von Wasser in diesen komplexen Netzwerken von Wasserstoffbrückenbindungen zu berücksichtigen, die für die Signalvermittlung in der Zelle von entscheidender Bedeutung sind."
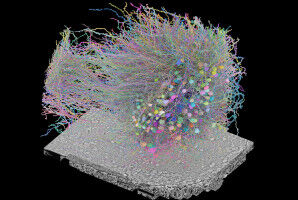
Im Zentrum dieser Bemühungen steht ein Computerdesign-Tool namens SPaDES. Die Wissenschaftler nutzten es, um synthetische GPCRs zu entwerfen. Beginnend mit dem Adenosinrezeptor A2A als Modell konzentrierten sie sich auf die Veränderung seiner "Kommunikationszentren", d.h. der Schlüsselstellen für die Interaktion zwischen Wassermolekülen und Aminosäuren. Diese Zentren fungieren als Schalttafeln, die Informationen über das gesamte Protein weiterleiten. Durch die Gestaltung von Netzwerken, die die Verbindungen durch Wasser optimieren, hat das Team 14 Rezeptorvarianten geschaffen.
Mithilfe der SPaDES-Software konnten sie simulieren, wie diese Veränderungen die Formen und Funktionen der Rezeptoren in verschiedenen kritischen Zuständen beeinflussen würden. Nach einem Computer-Screening synthetisierte das Team dann die vielversprechendsten Rezeptoren und testete ihre Aktivitäten in Zellen.
Das Ergebnis war bemerkenswert: Die Dichte der vom Wasser gestreuten Wechselwirkungen erwies sich als Schlüsseldeterminante für die Aktivität der Rezeptoren. Diejenigen mit der höchsten Anzahl an Wechselwirkungen zeigten eine größere Stabilität und eine höhere Signalwirkung. Das vielversprechendste Design, Hyd_high7 genannt, nahm sogar eine unerwartete und unvorhergesehene Form an und bestätigte die Designmodelle.
Die 14 neuen Rezeptoren haben ihre natürlichen Gegenstücke in vielerlei Hinsicht übertroffen, u. a. durch ihre Fähigkeit, bei hohen Temperaturen stabil zu bleiben, und ihre verbesserte Fähigkeit, Signalmoleküle zu binden. Diese Eigenschaften machen sie nicht nur funktionell überlegen, sondern auch robuster für die Wirkstoffentdeckung und die synthetische Biologie.
Diese Arbeit birgt ein großes Potenzial für die Medizin und die Biotechnologie. Da die neue Methode die präzise Gestaltung von Membranrezeptoren ermöglicht, könnte sie zu gezielteren Therapien für Krankheiten wie Krebs und neurologische Störungen führen. Über die Medizin hinaus könnten diese synthetischen Rezeptoren in Biosensoren oder anderen Werkzeugen zur Erkennung von Umweltveränderungen eingesetzt werden.
Die Ergebnisse stellen auch die klassischen Annahmen über die Funktionsweise der GPCRs in Frage, da sie eine unerwartete Flexibilität in ihren wasserdiffundierten Interaktionsnetzwerken aufzeigen. Dies eröffnet neue Perspektiven für die Erforschung eines bisher ungenutzten Potenzials dieser Proteine, sowohl in der Natur als auch im Labor.
Referenzen
Chen, K.-Y., Lai, J. K., Rudden, L. S. P., Wang, J., Russell, A. M., Conners, K., Rutter, M. E., Condon, B., Tung, F., Kodandapani, L., Chau, B., Zhao, X., Benach, J., Baker, K., Hembre, E. J., Barth, P. (2025). Computational design of highly signaling active membrane receptors through solvent-mediated allosteric networks. Nature Chemistry 23 January 2025. DOI: 10.1038/s41557-024-01719-2