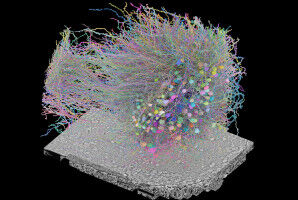
Alles Lebendige besteht aus Proteinen. Sie strukturieren die Zellen, versorgen sie mit Nährstoffen, heilen sie oder machen sie krank. Sie spielen auch eine Schlüsselrolle bei der Interaktion zwischen Medikamenten und dem Körper.
Heute stehen die Planeten in einer Reihe, um eine völlig neue Ära der Forschung einzuleiten. In der ersten Reihe stehen die generative künstliche Intelligenz, die neue Proteinformen erfinden kann, sowie neue bildgebende Verfahren wie die Röntgenkristallographie und die Kryo-Elektronenmikroskopie, die es ermöglichen, die Form und Zusammensetzung von Proteinen in der realen Welt mit beispielloser Genauigkeit zu beobachten. Im Zusammenspiel ermöglichen diese jüngsten Fortschritte die Vorstellung neuer Prozesse, die unter anderem zur Entwicklung innovativer biologischer Arzneimittel führen.
Sehr nahe an den Biomolekülen
Das Wissen über die Interaktion zwischen Proteinen und Zellen beruht heute weitgehend auf empirischen Daten, die in jahrelanger biomedizinischer Forschung gewonnen wurden. Die Rolle von Insulin bei der Verstoffwechselung von Glukose im Körper ist recht gut bekannt, um nur ein Beispiel zu nennen.Aber auch unzählige andere Interaktionen zwischen Proteinen und Zellen sind noch immer rätselhaft. Oder sind bei Fehlfunktionen die Ursache für Krankheiten, ohne dass man genau weiß, wie oder warum.
Das Wissen wächst jedoch exponentiell dank neuer Werkzeuge und Technologien. Die Kryo-Elektronenmikroskopie, die im Centre d’imagerie Dubochet auf dem Campus der UNIL-EPFL praktiziert und entwickelt wird, hat es beispielsweise ermöglicht, in vitro zu beobachten, wie das Spike-Protein der Omicron-Variante von SARS-CoV-2 mit dem menschlichen Rezeptor auf der Zelloberfläche interagiert. Dies ermöglicht es, sowohl die schnelle Ausbreitung des Virus im Körper als auch seine Immunität gegenüber den für die früheren Varianten entwickelten Impfstoffen zu verstehen.
Spike Viele haben den Namen dieses Proteins während der Covid-19-Epidemie entdeckt. Das Spike-Protein ist die Speerspitze, die es dem SARS-CoV-2-Virus ermöglicht, in einige unserer Zellen einzudringen. Das Spike-Protein bindet sich an ein Protein namens ACE2, das auf der Membran einiger Zellen (insbesondere der Zellen unseres Atmungssystems) vorhanden ist, wodurch das Virus in diese Zellen eindringen kann. Spike besteht aus drei identischen Ketten, die Ausstülpungen auf der Virushülle bilden.

Trotzdem ist Spike ein beliebtes Ziel für unser Immunsystem, um die Infektion zu bekämpfen. Mithilfe von Impfstoffen kann dieser Kampf verstärkt werden.
Zur Herstellung eines Impfstoffs gegen SARS-CoV-2 wurden mehrere Methoden angewandt. Bei einem der Ansätze synthetisierten die Wissenschaftler das Spike-Protein des Virus und reinigten es anschließend. Anschließend setzten sie diese Spike-Proteine auf einem Nanopartikel zusammen. Der Impfstoff wird subkutan verabreicht und bewirkt, dass unser Immunsystem Antikörper gegen das Spike-Protein bildet, das als fremder Erreger erkannt wird. Bei mRNA-Impfstoffen wird nicht das Spike-Protein selbst, sondern sein Bauplan in Form von mRNA verabreicht. Die Zellen produzieren dann selbst das Spike-Protein, und unser Immunsystem reagiert darauf mit der Bildung spezifischer Antikörper.
Deep Learning auf lebende Organismen angewendet
Diese Fortschritte im Bereich der Bildgebung gehen Hand in Hand mit den Fortschritten im Bereich des maschinellen Lernens, das auf die Biowissenschaften angewandt wird. Die Arbeiten im Zusammenhang mit dem Proteindesign wurden gerade mit dem Nobelpreis für Chemie 2024 ausgezeichnet. David Baker, der amerikanische Pionier der computergestützten Biologie, teilt sich diese Ehre mit Demis Hassabis (Ehrendoktor der EPFL) und John M. Jumper, den Mitbegründern von AlphaFold. Diese Software gilt als Referenz in diesem Bereich und wurde mehrfach bei internationalen Wettbewerben zur Vorhersage von Molekülstrukturen ausgezeichnet.Generatoren für Biomoleküle
Auch die EPFL ist stark im Bereich des Proteindesigns engagiert. Seit mehr als fünf Jahren nutzt das Labor für Proteindesign und Immunoengineering von Bruno Correia automatische Analysetechniken, um die Interaktionsfähigkeiten von Proteinen und ihren Rezeptoren vorherzusagen. "Die Anwendung von Deep Learning auf das Feld der biologischen Technik hat eine neue Ära eingeleitet", erklärt er.Diese Arbeiten tragen nicht nur zu einem besseren Verständnis der Funktionsweise von Lebewesen bei, sondern sind auch der Rohstoff für eine beginnende pharmazeutische Revolution. Die generative künstliche Intelligenz im Stil von ChatGPT kann, wenn sie sich von den Proteinen und molekularen Interaktionen ernährt, die AlphaFold und seine akademischen Gegenstücke enthüllt haben, unzählige noch nicht existierende Molekülformen entwerfen, sie modellieren und ihre Interaktionen mit den Zellen simulieren. Und das im Maßstab von Milliarden Berechnungen pro Sekunde, bis man theoretisch relevante Modelle für therapeutische Anwendungen gefunden hat. "Von diesem neuen Paradigma wird das gesamte Feld der Biotechnologie profitieren", versichert Bruno Correia.
Das gesamte Feld der Biotechnologie wird von diesem neuen Paradigma profitieren.
Bruno Correia
Von den Plänen zur Realität
Es gibt jedoch Möglichkeiten, bereits bekannte oder noch unveröffentlichte Proteine "auf Abruf" zu produzieren. Florence Pojer, die Leiterin der Proteinproduktions- und -strukturplattform der EPFL (PTPSP), macht genau das. In den Glasschränken dieses Zentrums werden Fläschchen mit rötlichem Inhalt mehrere Stunden lang geschüttelt. "Diese hier zum Beispiel sind HEK-Zellen aus der menschlichen Niere - unsterblich gemacht und seit Jahrzehnten gezüchtet. Wir verwenden sie, um Proteine wie Antikörper zu produzieren, nachdem wir sie mit Plasmiden transfiziert haben, die die gewünschte Sequenz enthalten", erklärt Florence Pojer. Andere zelluläre oder bakterielle "Suppen" können ebenfalls verwendet werden, je nachdem, welche Ergebnisse man anstrebt. Dann werden die Produktionen gereinigt, um die Zielproteine zu isolieren. "Im Prinzip kann man jedes Protein anhand seiner Gensequenz herstellen; derzeit kann jedoch nur ein sehr kleiner Teil der vom Computer in silico entworfenen Proteine tatsächlich produziert werden und funktionieren", erklärt Florence Pojer. Neue biotechnologische Ansätze versuchen, den Katalog dessen, was man in Zukunft herstellen kann, zu erweitern."Mehrere dieser innovativen Techniken werden an der EPFL angewandt oder weiterentwickelt. Dies ist der Fall bei dem bereits erwähnten Bruno Correia, aber auch bei Sebastian Maerkl, dessen Ansatz sich von den biologischen Prozessen in lebenden Zellen entfernt und in vitro auf der Grundlage der etwa 30 Enzyme arbeitet, die wirklich für die Herstellung von Proteinen erforderlich sind. Matteo Dal Peraro beschäftigt sich mit großen Molekülkomplexen und ihren Wirkungsmöglichkeiten, die durch ihre Struktur und Zusammensetzung bestimmt werden, indem er Beobachtung, Modellierung und Simulation miteinander verbindet.
Ein großes Konsortium im Visier
Bruno Correia und Beat Fierz von der EPFL arbeiten am Aufbau eines Konsortiums, das die Arzneimittelforschung in ein neues Zeitalter führen soll, das durch maschinelles Lernen beschleunigt wird. Durch die Zusammenführung der zahlreichen ergänzenden Arbeiten, die an den Hochschulen des Landes laufen, wird die Schweiz nicht nur zu einem Exzellenzzentrum in diesem Bereich werden, sondern auch die rasche Entstehung neuer, wirksamer Proteine zum Wohle der Patienten fördern. Es geht darum, die Entwicklung künstlicher Intelligenz für das Moleküldesign zu unterstützen, neue Konzepte für die Interaktion zwischen Medikamenten und lebenden Zellen zu entwerfen, neue Datenbanken zu schaffen, um die Effizienz der Designwerkzeuge weiter zu verbessern, und die neue Generation von Wissenschaftlern auf neue Forschungs- und Umsetzungsmöglichkeiten vorzubereiten. Ein ganzes Programm, das sicherlich Generationen von Wissenschaftlern begeistern wird.AlphaFold - Eigentum von Google DeepMind - ermöglicht es, aus der Liste der Aminosäuren, aus denen ein Protein besteht, eine sehr genaue Vorstellung davon zu gewinnen, wie das Protein in sich selbst "gefaltet" ist - ein Parameter, der seine Funktionen und die Fähigkeit, mit seiner Umgebung zu interagieren, bestimmt. Seit der dritten Version, die im Mai 2024 veröffentlicht wurde, kann die Software sogar die Struktur und die Interaktionen von DNA- und RNA-Strängen modellieren, was die genaue Identifizierung von Zellmechanismen ermöglicht, die für die Entwicklung neuer Medikamente entscheidend sind. Sie wurde der Gemeinschaft in einem Modus zur Verfügung gestellt, der es unzähligen Wissenschaftlern ermöglicht, sie für die Entwicklung neuer therapeutischer Moleküle zu nutzen.